颜宁团队合作最新Science
糖的化学复杂性以及非模板式的生物合成过程给建立序列-结构关系带来了巨大挑战。
2026年4月23日,深圳医学科学院/深圳湾实验室颜宁,清华大学黄隽豪及闫创业共同通讯在Science 在线发表题为“Structural N- and O-glycans revealed by high-resolution cryo-EM analysis of tubular mastigonemes”的研究论文,该研究报告了来自金藻物种Ochromonas danica的管状鞭毛体的冷冻电子显微镜结构,这些结构的分辨率为 1.8 - 2.2 埃。
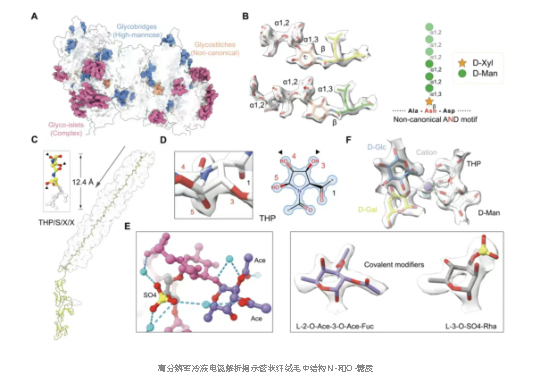
在高半乳糖型和复杂 N-糖链之外,该研究还发现了一个在 Ala-Asn-Asp(AND)基序上的非标准 N-糖链。表面突起由密集的 O-糖链覆盖着 PSXX 四肽重复序列,每个重复序列上有两个糖链连接在三羟基脯氨酸上,还有一个在丝氨酸上。除了各种类型的糖及其共价修饰物之外,水分子(占已解析体积的 10%以上)和阳离子也清晰可见,并且它们介导了结构的组装。总之,该研究为研究高阶生物组装中的糖折叠提供了框架。

在生命科学领域,糖类(碳水化合物)是最后一个尚未被完全破译的“暗物质”。它们不仅提供能量,更在细胞识别、免疫反应、信号传导等核心生命过程中扮演关键角色。然而,由于其结构的极端复杂性、高度柔性和非模板化合成的特性,科学家一直难以在天然状态下解析其高分辨率三维结构,极大地限制了对糖类生物学机制的深入理解。
研究团队将目光投向了单细胞藻类Ochromonas danica 的鞭毛体毛(一种细胞表面的丝状附属结构),利用冷冻电子显微镜(cryo-EM)技术,成功解析了其鞭毛体毛中一种管状结构(T型鞭毛体毛)的近原子分辨率(1.8-2.2埃)三维结构。这一成就如同为糖类世界开启了一台“电子显微镜”,首次以前所未有的清晰度窥见了天然糖复合物的精密构造。
技术革命:当冷冻电镜遇见AI建模
研究的突破首先源于方法学的融合创新。面对糖链结构建模的“噩梦级”挑战,团队开发了名为 EModelG 的人工智能(AI)自动化建模管道。这个“AI助手”能够高效、准确地根据cryo-EM获得的高分辨率三维密度图,自动构建糖链的原子模型。结合质谱化学分析进行验证,这套综合工作流程解决了长期困扰糖生物学的结构解析难题。
核心发现:糖类结构的“工具箱”与“脚手架”
在惊人的分辨率下,研究揭示了T型鞭毛体毛的分子蓝图,带来三大关键发现:
-
多样化的糖链“工具箱”:结构图清晰地展示了多种类型的N-连接和O-连接糖链,包括一种非标准形式的N-糖链。特别重要的是,研究者首次在近原子分辨率下直接“看见”了阿拉伯糖残基及其5‘,5‘-磷酸二酯键,这种键如同“分子订书钉”,将相邻糖链交联成稳定的晶格结构,阐明了糖链组装成高级结构的化学基础。
-
未知蛋白质的“骨架”:结构解析出两种此前完全未知的糖蛋白。其中一种蛋白骨架呈现出规律性的重复序列,被特定的O-糖链修饰,被命名为“PSXX型”糖纤维。这为理解糖蛋白如何作为“脚手架”支撑复杂糖结构提供了模板。
-
结构与功能的关键“介质”:高分辨率图谱还揭示了一个广泛且高度有序的水分子网络,其体积占整个结构模型的10%以上。这些水分子并非无序存在,而是构成了稳定结构与行使功能所必需的氢键网络,是理解糖类生物功能的又一关键。
深远意义:确立新模式与打开新视野
这项研究的意义超越了一个特定结构的解析。它成功将奥克罗莫纳斯·丹卡确立为研究“糖类的序列-结构-功能关系”的理想模式生物。更重要的是,它所建立并验证的“高分辨冷冻电镜成像 + AI自动化建模 + 质谱验证”综合工作流程,为系统性解析各种复杂天然糖类结构铺平了道路。这项突破性进展,标志着糖生物学正从“化学组成分析”迈入“高分辨率结构生物学”的新时代,为未来开发基于糖结构的药物、疫苗和生物材料奠定了坚实的分子基础。
深圳医学科学院创始院长、深圳湾实验室主任颜宁,清华大学生命学院博士生黄隽豪、副教授闫创业为本文的共同通讯作者。黄隽豪、水木学者陶慧、陈晟为本文共同第一作者。科研助理崔亚华、博士生徐艺然为研究工作做出了重要贡献。深圳医学科学院生物结构解析平台、高性能计算平台提供了电镜数据采集和计算支撑。实验的质谱鉴定工作得到了清华大学蛋白质化学与组学平台、深圳医学科学院人类免疫学研究所盛心磊研究员的支持。本研究得到了国家自然科学基金“破译生命的糖质密码”重大研究计划,国家自然科学基金青年学生基础研究项目,北京生物结构前沿研究中心与清华-北大生命科学联合中心的经费支持。同时,特别感谢鹏瑞基金会捐赠的“迈瑞教授”经费对颜宁研究工作给予的支持。
参考消息:
https://www.science.org/doi/10.1126/science.aef4958
赞一个
更有众多热门



















